很多团队刚开始做单细胞项目时,第一反应都是先找流程、找软件、找教程。真跑起来以后才发现,卡住进度的往往不是分析方法,而是机器不够用。样本一多、细胞数一上来,内存不够、存储太慢、多人抢资源这些问题会一起冒出来。
这篇文章不讲空泛的“高性能服务器”,而是从真实项目角度讲清楚:单细胞分析服务器到底怎么配,什么地方最值得优先花预算。
单细胞分析最吃什么资源
不同阶段,对硬件的依赖并不一样。
原始数据处理阶段
如果你从 FASTQ 开始,尤其要跑 Cell Ranger 这类工具生成表达矩阵,通常更吃:
CPU 线程数
内存
磁盘读写速度
下游分析阶段
进入 Seurat、Scanpy、聚类和注释之后,资源压力往往更多落在:
内存
存储容量
多用户并发能力
所以,单细胞分析服务器配置不能只盯 CPU。对多数团队来说,内存往往才是第一个真正撞上的瓶颈。
CPU 怎么选
如果你的工作主要是常规单细胞分析、批量跑几个样本、做基础整合和下游分析,CPU 不一定要堆得特别夸张,但至少别让预处理阶段慢得太离谱。
一般可以这样看:
入门或轻量使用:16 核左右
常规实验室使用:24 到 32 核
多项目并发或服务型团队:32 核以上更稳
如果只是单人偶尔跑数据,16 核机器已经能做不少事;但如果实验室里几个人共用一台服务器,24 核以上通常会轻松很多。
内存怎么配
在单细胞分析服务器配置里,内存通常比 CPU 更关键。尤其是下面这些场景:
细胞数达到数万到十几万
需要做多样本整合
需要同时开多个对象或多个会话
要跑复杂下游分析
可以粗略按下面这个量级估算:
小型练手或教学用途:64 GB
常规项目分析:128 GB
多样本整合或较大项目:256 GB
服务团队或大队列项目:512 GB 及以上
如果预算只能优先保证一个指标,我更建议先保内存,而不是一味追更高主频。
存储怎么配
很多人只看表达矩阵大小,低估了原始数据、临时文件、中间结果和备份的占用。真实项目里的存储消耗,通常来自这几部分:
原始测序数据
中间处理文件
最终结果文件
历史项目归档
比较稳的做法是至少分两层:
系统盘或高速盘:放运行环境和当前活跃项目
大容量数据盘:放原始数据和归档结果
如果条件允许,优先选 NVMe SSD 作为活跃项目盘。单细胞分析里不少步骤会受磁盘 IO 影响,并发时尤其明显。
GPU 要不要配
这是经常被问到的问题,但答案并不总是“要”。
对大多数基于 Seurat、常规 R/Python workflow 的单细胞分析来说,GPU 不是刚需。多数基础分析还是以 CPU 和内存为主。
只有在下面这些场景里,GPU 价值才更明显:
深度学习相关单细胞模型
大规模表示学习或多组学模型
特定加速框架明确依赖 GPU
如果你的主要目标是日常 scRNA-seq 分析,预算有限时,优先把钱放在内存和高速存储上,通常更划算。
本地服务器还是云服务器
这取决于项目节奏和团队使用方式。
更适合本地服务器的情况
实验室长期有稳定项目
数据量持续增长
团队多人需要共享环境
对数据留存和内部管理要求较高
更适合云服务器的情况
项目是阶段性需求
高峰期资源波动大
暂时不想一次性投入硬件采购
需要临时扩容处理大项目
如果你是刚起步的小团队,一个相对稳妥的策略是:先在云上验证真实需求,再决定是否采购本地机器。
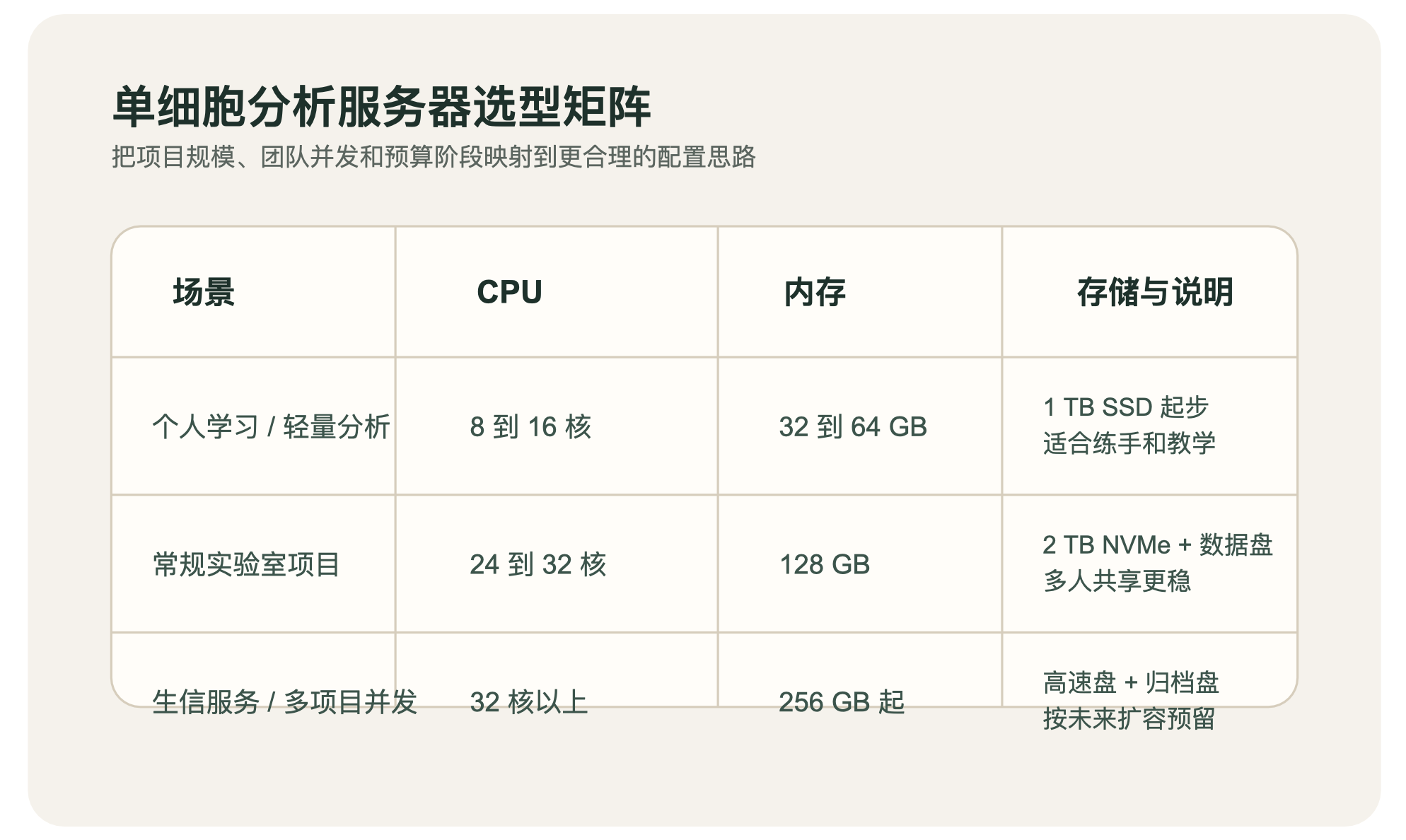
给不同团队的配置建议
1. 个人学习或轻量分析
CPU:8 到 16 核
内存:32 到 64 GB
存储:1 TB SSD 起步
适合教学、练手和小型数据集分析。
2. 常规实验室单细胞项目
CPU:24 到 32 核
内存:128 GB
存储:2 TB NVMe SSD + 4 TB 以上数据盘
这是很多实验室比较均衡的一档。
3. 生信服务团队或多项目并发
CPU:32 核以上
内存:256 GB 起
存储:2 到 4 TB 高速 SSD + 更大容量归档盘
如果同时服务多个课题组,这一档通常会省心很多。
采购前,先把这 5 个问题问清楚
如果你准备把单细胞分析服务器真正落地,不管是内部采购、做方案比较,还是找供应商沟通,建议先把下面 5 个问题整理清楚:
你的项目通常从哪里开始,是
FASTQ、矩阵还是对象文件未来 6 到 12 个月,样本数、细胞数和并发人数大概会增长到什么水平
你主要是单人使用,还是实验室或团队共享,是否会同时跑多个项目
你更在意一次性采购成本,还是长期稳定性、扩展性和管理便利性
你是否需要长期留存脚本、环境、结果文件和原始数据
这些问题决定的不是“参数表写多大”,而是整套环境该怎么配。
哪些情况更适合做定制化方案
如果你遇到下面这些情况,通常不太适合照着一张通用配置表直接下单:
项目类型差异大,既有单细胞也有 bulk RNA-seq 或其他组学任务
团队里会同时有多个人跑分析,资源争抢明显
需要同时兼顾活跃项目、高速盘和历史归档
还没完全确定本地部署还是云上混合部署
希望未来 1 到 2 年还能继续扩容
这种情况下,更稳的思路是先按工作流和数据规模估算需求,再倒推 CPU、内存、存储和部署结构。
单细胞分析服务器配置常见问题
单细胞分析服务器最优先升级什么
多数情况下先看内存,其次看高速存储。CPU 当然重要,但很多团队真正卡住的是大对象进内存和磁盘 IO。
本地电脑能不能跑单细胞分析
中小型数据可以,尤其是学习和练手阶段。但一旦进入多样本整合、较大细胞量级或多人协作,本地机器很快会吃力。
单细胞分析一定要买 GPU 服务器吗
不一定。对大多数常规 scRNA-seq workflow 来说,GPU 不是必需项。
![生信分析跑不动?试试稳定高性价比的生信云 → [www.tebteb.cc]](https://www.tebteb.cc/upload/%E7%94%9F%E4%BF%A1%E5%9C%86%E6%A1%8C-kgzw.png)